国家现代农业产业技术体系四川创新团队信息服务平台
Information service platform for Sichuan innovation team of national modern agricultural industry technology system
小麦穗发芽(pre-harvest sprouting,PHS)是指小麦在成熟期遭遇连续阴雨天气时籽粒在穗上发芽的现象。小麦穗发芽是基因与环境互作的结果,涉及众多的影响因素,包括种子休眠水平、种子结构、植物激素等内部因素,以及温度、湿度等外界环境因素,其中,种子自身的休眠特性是影响穗发芽的主要因素。近期,四川农业大学王际睿课题组完成的题为“小麦穗发芽抗性机制及抗性育种研究”的研究在《中国农业科学》2024年第57卷7期正式发表。

种子休眠水平是影响小麦穗发芽抗性的主要因素,而往往驯化作物的籽粒休眠水平低,导致栽培小麦普遍比其野生祖先种更易发生穗发芽。小麦穗发芽主要受外源环境(温度、湿度等)和内源植物激素(GAs、ABA、IAA、MeJA、ET、BR)的调控。已鉴定出一批抗穗发芽材料,并克隆了一系列调控穗发芽抗性的关键基因,如PM19、MFT、MKK3、Myb10-3D、Vp1等。通过分子标记辅助选择、人工合成小麦和 CRISPR/Cas9 基因编辑技术,已成功创制了抗穗发芽小麦新材料。

穗发芽相关基因在小麦种子发育的不同时期表达模型
该文主要从穗发芽发生的遗传与生理机制、穗发芽对产量品质的危害、穗发芽抗性种质资源与相关基因发掘、抗穗发芽小麦新材料创制等方面综述近年来小麦穗发芽的研究进展,并对未来小麦抗穗发芽研究方向和育种改良策略提出建议,以期为未来创造环境稳定的抗穗发芽小麦品种提供参考。
该研究获得科技创新 2030(2023ZD04069)、国家农业科技重大专项(NK20220607)、国家自然科学基金(32301810,32301837,U22A20472)、国家重点研发计划(2018YFE0112000)、四川省科技计划(2023NSFSC0217,2021YFH0077)的资助。
2024年3月6日,BMC Genomics在线发表了四川农业大学周永红和张海琴课题组题为“A chromosome level genome assembly ofPseudoroegnerialibanoticareveals a keyKcsgene involves in the cuticular wax elongation for drought resistance”的研究成果。

小麦族是禾本科植物中十分重要的一个类群,其中包含了小麦、大麦、黑麦等主要粮食作物,也包含了冰草属、披碱草属、拟鹅观草属等许多重要的牧草资源。拟鹅观草属(PseudoroegeriaÁ. Löve)是1980年由Löve根据染色体组组成建立的一个新属,其染色体组为St,有二倍体和四倍体,St基因组参与了小麦族8个属150余种的物种形成,是小麦族中最重要的基本基因组之一。拟鹅观草属植物广泛分布于干旱/半干旱地区,因此具良好的干旱适应性。拟鹅观草属植物是优良的牧草资源,且是小麦的三级基因源,可用作麦类作物抗旱性遗传改良的来源。
本研究采用二代Illumina +三代Nanopore的策略对拟鹅观草进行深度测序,结合Hi-C技术辅助组装基因组,首次获得了高质量拟鹅观草参考基因组。结果表明,拟鹅观草基因组大小为2.99 Gb,contig N50长度为0.96 Mb,super scaffold N50为398.55 Mb,GC含量为45.07%,。注释得到46,369个编码基因,重复序列占比71.62%。通过Hi-C技术将2.75 Gb的scaffold序列锚定于7条染色体上,占总基因组大小的92.09%。染色体大小在327.30 Mb (Chr4) ~ 464.04 Mb (Chr2)之间(图1)。
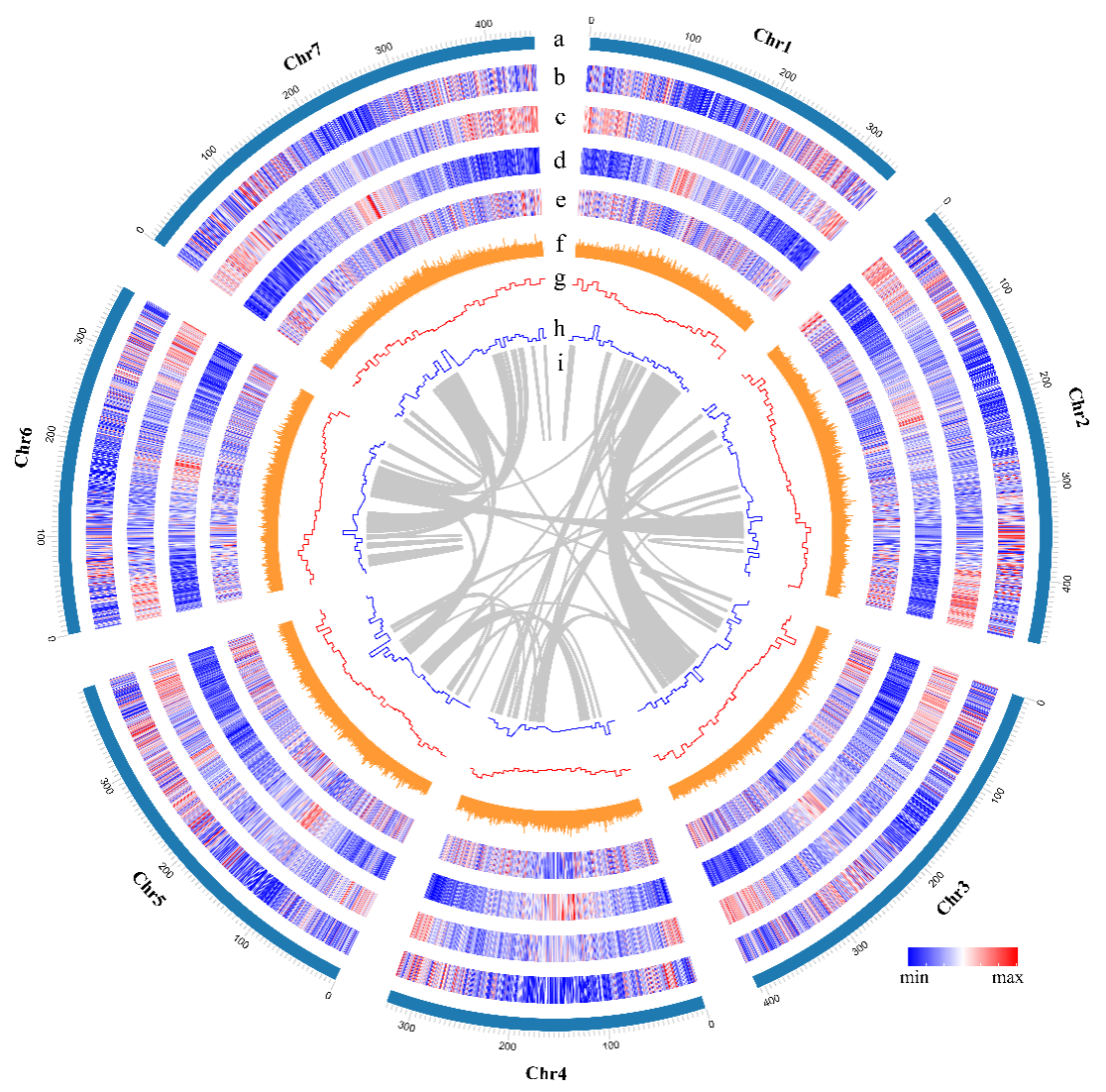
图1拟鹅观草基因组特征
从外向内依次是:a:染色体(Chr1-7)名称和大小;b:基因密度;c:重复序列密度(窗口大小500 Kb);d:LTR Gypsy(窗口大小500 Kb);e:LTR Copia(窗口大小500 Kb);f:GC含量(%);g:扩张基因(窗口大小10Mb);h:收缩基因(窗口大小10Mb)。i:染色体同源关系。
为了探索St基因组的系统发育和分化,使用14个物种共享的单拷贝直系同源基因进行系统发育分析并构建系统发育树。结果显示:高粱和玉米是C4植物,在系统发育树上首先分化出来,之后水稻、二穗短柄草和鸭茅相继分化出来。小麦族物种在系统发育树上聚在一支,拟鹅观草在距今约10.7百万年前出现,晚于大麦(约11.9百万年前)且早于黑麦(约9.6百万年前)分化出来(图2A)。
基因家族的聚类分析结果显示:14个物种的18个(亚)基因组一共聚类出28,260个基因家族,共有基因家族为5383个,其中各个物种共有的单拷贝基因家族为744个(图2-12A)。提取节节麦、中国春、大麦、黑麦、拟鹅观草基因组相应的聚类结果,绘制韦恩图(图2C),从Venn图中可见,相对于其它物种,拟鹅观草有1078个特异的基因家族(包含1078个基因)。
全基因组复制(WGD)事件指植物在进化过程中发生的全基因组水平的重复事件,在植物基因组中广泛存在,被认为是植物基因组进化的重要推动力量。为了确认拟鹅观草基因组是否存在全基因组复制事件,对拟鹅观草、鸭茅和二穗短柄草基因组的同义替换率(Ks)进行计算。结果显示:Ks峰值为0.20,出现在拟鹅观草与鸭茅分化峰值(0.05)和拟鹅观草与二穗短柄草分化峰值(0.05)之后,表明在禾本科的共同祖先中发生了全基因组复制事件(图2B)。
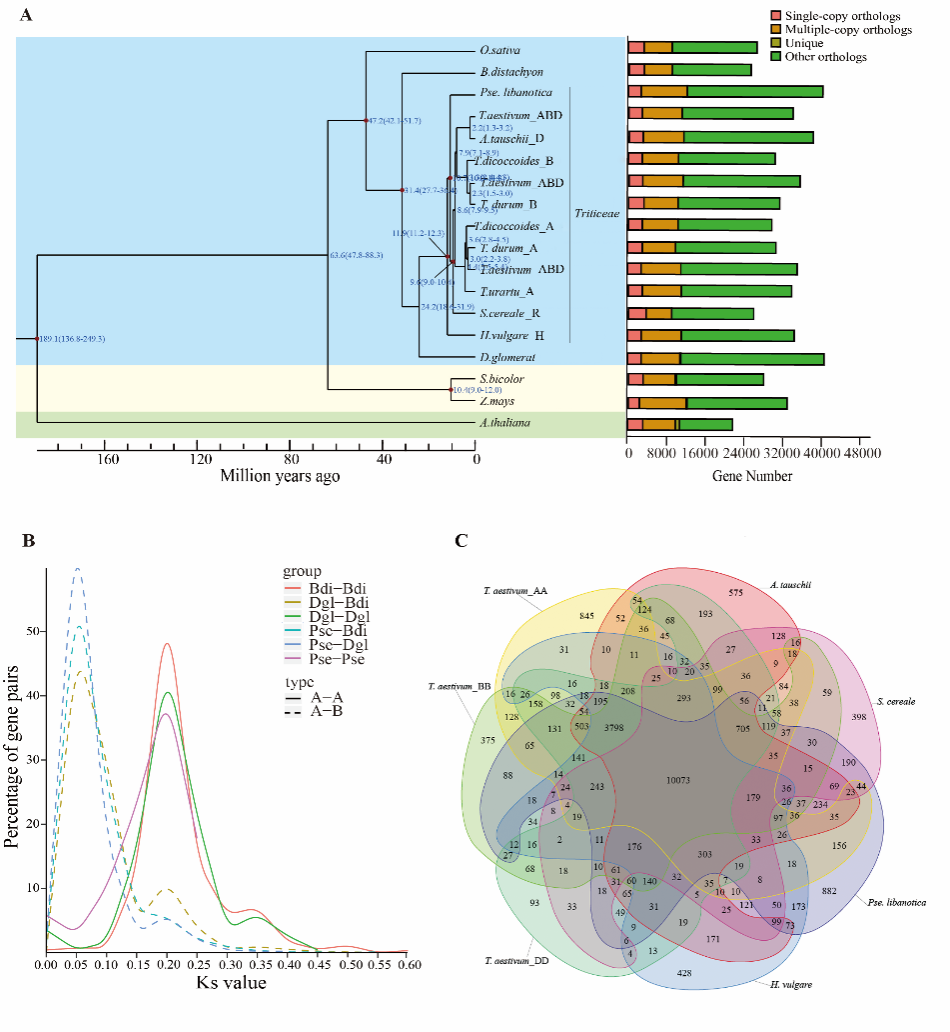
图2拟鹅观草基因家族与基因组进化
通过拟鹅观草干旱胁迫下的转录组数据分析,鉴定出14个和角质层蜡质合成相关的基因,包含19个转录本。其中包括1个乙酰辅酶A羧化酶(ACC)基因、1个脂酰-酰基载体蛋白硫酯酶B(FatB)基因、10个酮脂酰基辅酶A合酶(KCS)基因、4个脂肪酰基辅酶A还原酶(Facr)基因、2个醛脱羰基酶(Cer)基因和1个P450依赖性酶(CYP)基因。它们共同作用赋予拟鹅观草一定的抗旱性。
在脂肪酸合成途径中,Acc和Fatb在干旱胁迫期间表达上调。在脂肪酸延长过程中,Kcs5.1、Kcs5.2和evm.TU.CTG175.54基因表达显著上调,其他Kcs基因表达显著下调。催化超长链脂肪酸合成包括脂肪醇合成过程(Facr)和烷烃合成过程(Cer和CYP96A15),其中,仅有Farc1.1在干旱胁迫期间下调表达,其余基因均上调表达(图3)。综上,推测Kcs5.1、Kcs5.2和evm.TU.CTG175.54是调控拟鹅观草角质层中脂肪酸延长的主要因子。
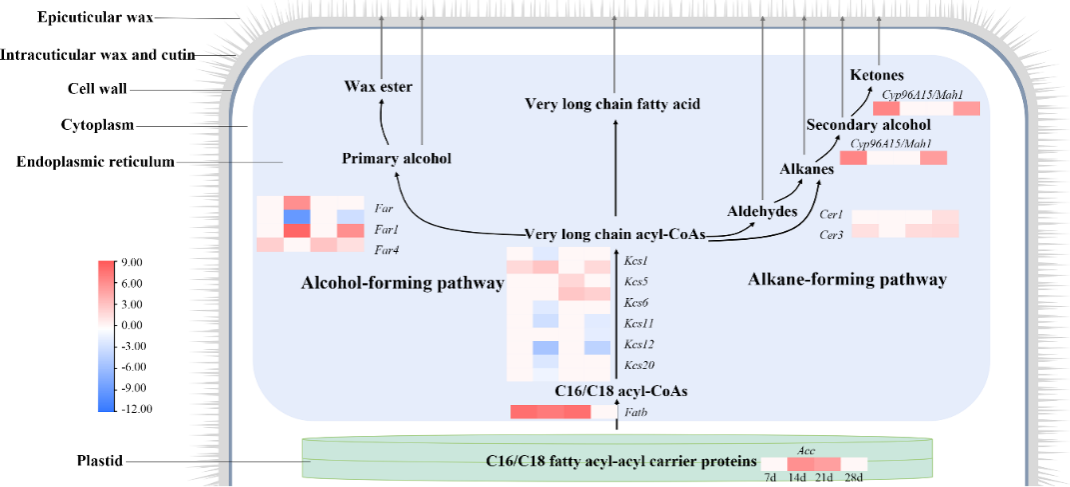
图3拟鹅观草干旱胁迫下角质层蜡质生物合成途径相关基因的表达量变化
本研究为拟鹅观草基因组学研究奠定了重要基础。同时丰富了小麦族物种的基因资源库,并且为解析拟鹅观草抗旱分子机制提供了有价值的信息。
四川农业大学小麦研究所在读博士翟星光、吴丹丹博士和陈晨为本论文的共一作者。四川农业大学小麦研究所周永红教授和草业科技学院张海琴教授为本论文共同通讯作者。本研究得到了国家自然科学基金(32270388;32200180)和四川省科学技术厅(23NSFSC1995)的支持。
原文链接:https://bmcgenomics.biomedcentral.com/articles/10.1186/s12864-024-10140-5
2024年2月26日,The Plant Journal 在线发表了四川农业大学王际睿课题组题为“Variation of TaMyb10 and their function on grain color and pre-harvest sprouting resistance of wheat”的研究成果。

穗发芽(Pre-harvest Sproutin)是禾本科作物成熟但未收获的籽粒在高温高湿环境下穗上发芽的现象,造成产量与质量大幅度下降。参与小麦抗穗发芽基因中,PHS-3D(TaMyb10-D)起着至关重要的作用。前期该课题组利用人工合成六倍体SHW-L1(红粒,抗穗发芽)与栽培品种川麦32(白粒、感穗发芽)杂交构建高代RILs群体,定位到qPHS.sicau-3D位点,解释42.47%的表型变异,且qPHS.sicau-3D与调控籽粒颜色R位点相近(Yang et al.,2019)。进一步,通过精细定位、基因功能研究、转录组学和代谢组学分析表明,TaMyb10-D编码类黄酮代谢途径(籽粒红色基因R)和ABA合成途径(抗穗发芽基因PHS-3D),实现“一因多效”的作用,阐明了小麦籽粒颜色和发芽率的内在联系(Lang et al.,2021)。
本研究对416份面包小麦和302份节节麦的TaMyb10基因序列变异进行分析,鉴定出3个PAV变异和8个SNP变异。61.3%的种质资源在TaMyb10-A序列中存在214~305个碱基的缺失;79.3%的种质资源在TaMyb10-B序列第三外显子区域具有19个碱基的缺失;40.8%的种质资源由于3D染色体上缺乏2.4 Mb的片段(插入/缺失突变),导致该区段的TaMyb10-D/PHS-3D缺失。3个PAV变异和8个SNP变异共产生13种基因型,其中4种基因型具有PAV变异导致不能编码成熟蛋白,剩下的9种基因型编码5种成熟蛋白类型,尽管5种蛋白类型具有序列变异,但五种不同的蛋白质类型在结合下游基因(CHS,DFR和NCED)启动子方面具有相似的功能。TaMyb10-A、TaMyb10-B和TaMyb10-D在调控籽粒颜色和穗发芽抗性中具有功能冗余。
1. 面包小麦和节节麦中TaMyb10 CDS序列变异
小麦是异源多倍体,具有A、B、D三个基因组。对416份小麦和302份节节麦中Myb10的CDS序列进行分析,鉴定出3个PAV变异和8个SNP变异。针对这些变异,成功开发三个STS标记和4个KASP标记。这些变异共产生13种基因型,其中4种基因型具有PAV变异导致不能编码成熟蛋白,剩下的9种基因型编码5种成熟蛋白类型。
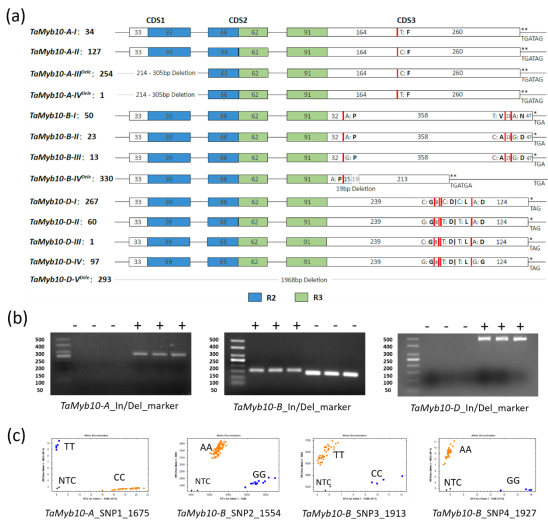
图1 TaMyb10序列变异和标记开发
2. TaMyb10不同基因组地理分布
对416份小麦品种进行地理分布分析,TaMyb10-A-IIIDele、TaMyb10-B-IVDele和TaMyb10-D-VDele基因型在小麦种群中占主导作用。
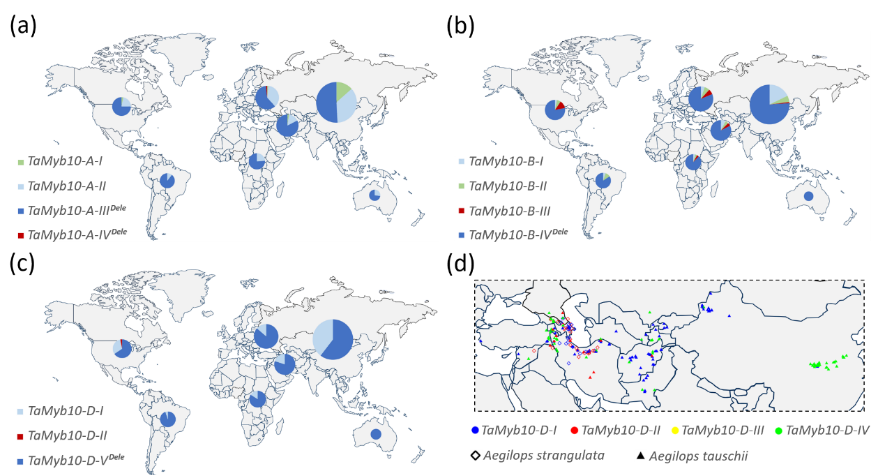
图2 TaMyb10 不同基因型地理分布
3. TaMyb10五种蛋白类型在类黄酮和ABA途径中与下游基因的结合功能
通过分析TaMyb10-D-I过表达(OE)株系转录组数据,鉴定到21个类黄酮合成途径上调基因,这些被认为是TaMyb10激活的候选基因。酵母单杂结果表明,TaMyb10-D-Pro I激活CHS-7500、CHS-7700、CHS-8400、CHS-8700、DFR-7900、DFR-8000启动子区域。且TaMyb10-A-Pro I、TaMyb10-B-Pro I、TaMyb10-A-Pro II和TaMyb10-D-Pro II蛋白类型具有相似的功能。
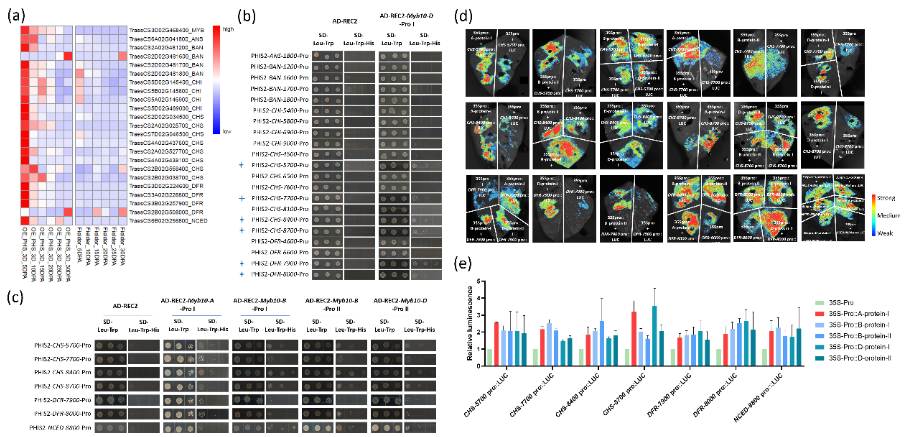
图 4 TaMyb10高度保守氨基酸序列绑定激活下游基因启动子
4. TaMyb10的保守序列调控下游基因
五种TaMyb10蛋白序列一致性为95.32%,在C端序列中分离出三个高度保守的片段,以评估TaMyb10的C端结构域残基是否能够与下游基因的启动子结合。酵母单杂结果表明,187-215的氨基酸结构域对CHS-7700和DFR-7900启动子的结合能力;147-163的氨基酸结构域对CHS-8700、DFR-7900和NCED-8800启动子的结合能力;221-231的氨基酸结构域对CHS-8400和DFR-8000启动子的结合能力。上述结果表明,激活区域的氨基酸序列高度保守,导致TaMyb10的五种蛋白可以结合并激活下游基因。

5. TaMyb10与籽粒颜色和发芽率的关系
为了评估TaMyb10在A、B和D基因组对种子发芽率(GPs)和谷物颜色的调节影响,选择了六份具有明显TaMyb10组合差异材料进一步研究。JiangXiZao和Mocho Cabecudo在A、B和D基因组都具有完整的TaMyb10。Chuanmai104在A和D基因组具有完整的TaMyb10;Chinese Spring(CS)只在D基因组中具有完整TaMyb10;Shumai580和Fielder在A、B和D基因组都缺乏完整的TaMyb10。下游基因(除DFR-8000以外)在不含有完整TaMyb10基因型的材料SM580和Fielder表达较低或者不表达,在含有任何完整TaMyb10基因型材料中正常表达。
对229个小麦品种评估TaMyb10、种子颜色和穗发芽(PHS)抗性之间的关系。150份材料具有TaMyb10-A-IIIDele、TaMyb10-B-IVDele和TaMyb10-D-VDele基因型,平均GPs为84.31%。23份材料只含有完整TaMyb10-A,平均GPs为73.81%。6份材料只包含完整TaMyb10-B,平均GPs为79.86%。4份材料只包含完整的TaMyb10-D,平均GPs为24.30%。13份材料在A、B和D基因组含有完整TaMyb10基因型,平均GPs为30.43%。TaMyb10-A、TaMyb10-B和TaMyb10-D对表型变异贡献率分别为4.36%、10.29%和37.32%。这些结果表明,TaMyb10的功能作用在不同品种中是普遍适用。
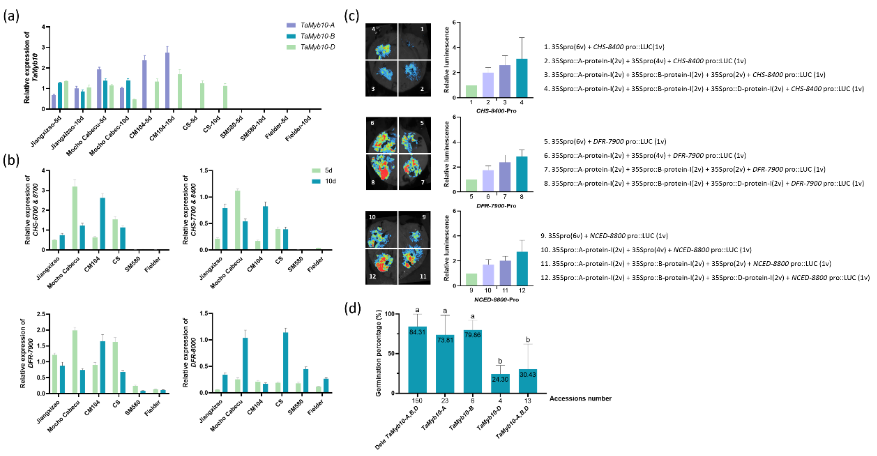
图5 TaMyb10与籽粒颜色和发芽率的关系
本研究通过序列变异分析、功能研究、表型变异分析,增进了对Myb10的序列变异和功能分化的理解,为小麦的穗发芽抗性提供了必要的资源。
四川农业大学小麦研究所在读博士郎静为本论文的第一作者。本研究得到了中国科技创新2030重大项目(2023ZD04069)、国家农业科技成果转化资金(NK20220607)、国家自然科学基金(U22A20472;32301837;32301810)、国家重点研发计划(2018YFE0112000)、四川省科技支撑计划(2021YFH0077;23NSFSC0770)、成都市科技支撑计划(2021-GH03-00002-HZ)和国家人类遗传资源共享服务平台开放基金(SKL-ZD202212)支持。
近年来,随着生活水平的提高,肥胖症、糖尿病和肠道疾病发生的几率显著增加。抗性淀粉具有降低血糖血脂、预防直肠癌等肠道和心脑血管疾病等多种保健功能,是理想的膳食来源。大麦是世界第四大禾谷类粮食作物,是藏族同胞的主粮。大麦籽粒中淀粉约占50%-70%,高抗性淀粉含量大麦可用作功能性和健康食品的重要原料。然而常规栽培大麦抗性淀粉含量较低不利于其在功能性食品生产上的应用。以CRISPR/Cas9系统为代表的基因组编辑工具有着简易、高效和精准的特性,为通过遗传修饰创制高抗性淀粉大麦提供了关键技术支撑。
该研究利用CRISPR/Cas9多基因编辑技术对部分编码大麦可溶性淀粉合成酶、淀粉分支酶等多个淀粉合成关机键基因进行靶向敲除。通过后代基因型鉴定得到了多种不同基因型的单基因、多基因缺失突变体,通过突变体籽粒组成及淀粉特性分析解析大麦淀粉合成酶基因及其互作对抗性淀粉合成的作用机制,相关成果“Genome editing of five starch synthesis genes produces highly resistant starch and dietary fibre in barley grains”发表在国际著名学术期刊《Plant Biotechnology Journal》。

该研究通过一次遗传转化在大麦中完成了对SSIIa、SSIIIa、SSIVa、SBEIIa、SBEIIb基因的靶向敲除。通过突变体后代自交分离鉴定获取了ssIIa、ssIIIa、ssIVa、sbeIIa、sbeIIb五个单基因缺失突变体,ssIIassIIIa、ssIIassIVa、sbeIIasbeIIb、ssIIassIIIassIVa、ssIIasbeIIasbeIIb五个多基因缺失突变体。籽粒组成测定结果显示,不同基因型突变体在抗性淀粉等健康有益成分含量上表现突出。其中,sbeIIasbeIIb和ssIIasbeIIasbeIIb突变体中抗性淀粉含量约为对照材料的35倍;ssIIassIIIa和ssIIassIVa突变体中抗性淀粉含量约为对照材料的10倍;sbeIIa和ssIIassIIIassIVa突变体中抗性淀粉含量分别约为对照材料的7倍和2倍;ssIIa、ssIIassIIIa、ssIIassIVa、sbeIIasbeIIb、ssIIassIIIassIVa、ssIIasbeIIasbeIIb突变体中果聚糖含量显著高于对照;ssIIa、ssIIIa、ssIIassIVa、ssIIassIIIassIVa、ssIIasbeIIasbeIIb突变体中β-葡聚糖含量显著高于对照;ssIIa、ssIIIa、ssIIassIIIa、ssIIassIVa、sbeIIasbeIIb、ssIIassIIIassIVa、ssIIasbeIIasbeIIb突变体中的纤维素含量显著高于对照。通过突变体淀粉特性分析,研究人员发现不同突变体在淀粉粒形态和组成、膨胀度、热力学特性、链长分布等参数上存在较大差异。综上所述,该研究创制了高抗性淀粉大麦新种质,解析了大麦淀粉合成酶基因及其互作对抗性淀粉合成的作用机制,为健康功能大麦培育提供了理论依据和技术支撑。
小麦研究所已毕业博士研究生杨强为该文第一作者,我所江千涛教授、澳大利亚Commonwealth Scientific and Industrial Research Organisation 李忠谊研究员为该文通讯作者。该研究得到四川省国际科技合作项目(2023YFH0041)的支持。
原文链接:https://onlinelibrary.wiley.com/doi/10.1111/pbi.14324
COPYRIGHT©四川省农业科学院农业信息与农村经济研究所 Add:成都市锦江区净居寺路20号附101号 蜀ICP备:20110305号 E-mail:scnycxtd@163.com建议使用chrome,firefox或者IE 11以上浏览器
